Inno-ADMET
1. Inno-ADMET 概述
ADMET 模块主要用于系统的评价药物的吸收、分布、代谢、排泄和毒性性质,也包括一些理化性质和药物化学性质。众多研究表明早期的 ADMET 性质评价可显著地提高药物研发的成功率。针对不同的需求,系统提供了两个不同的模型来计算成药性性质,分别为基于预训练的 MERT 模型和基于 GNN 子结构可解释性的 MGA 模型。基于自主收集的高质量数据,这两个模型均可实现 17 种物化性质、5 种药物化学性质、6 种类药性规则、33 种 ADME 性质、26 种毒性性质的系统性评价。从模型评估指标的角度来说,MERT 模型更为优秀,根据模型能否提供子结构对预测结果的影响上判断,MGA 模型更具优势,用户可根据自己的需要去选择相应的计算模型。
2. 使用说明
用户只需要四个步骤就可以完成计算:选择方法(默认选择 MERT)-确定输入方式-任务命名(可忽略)-提交任务(必点)。
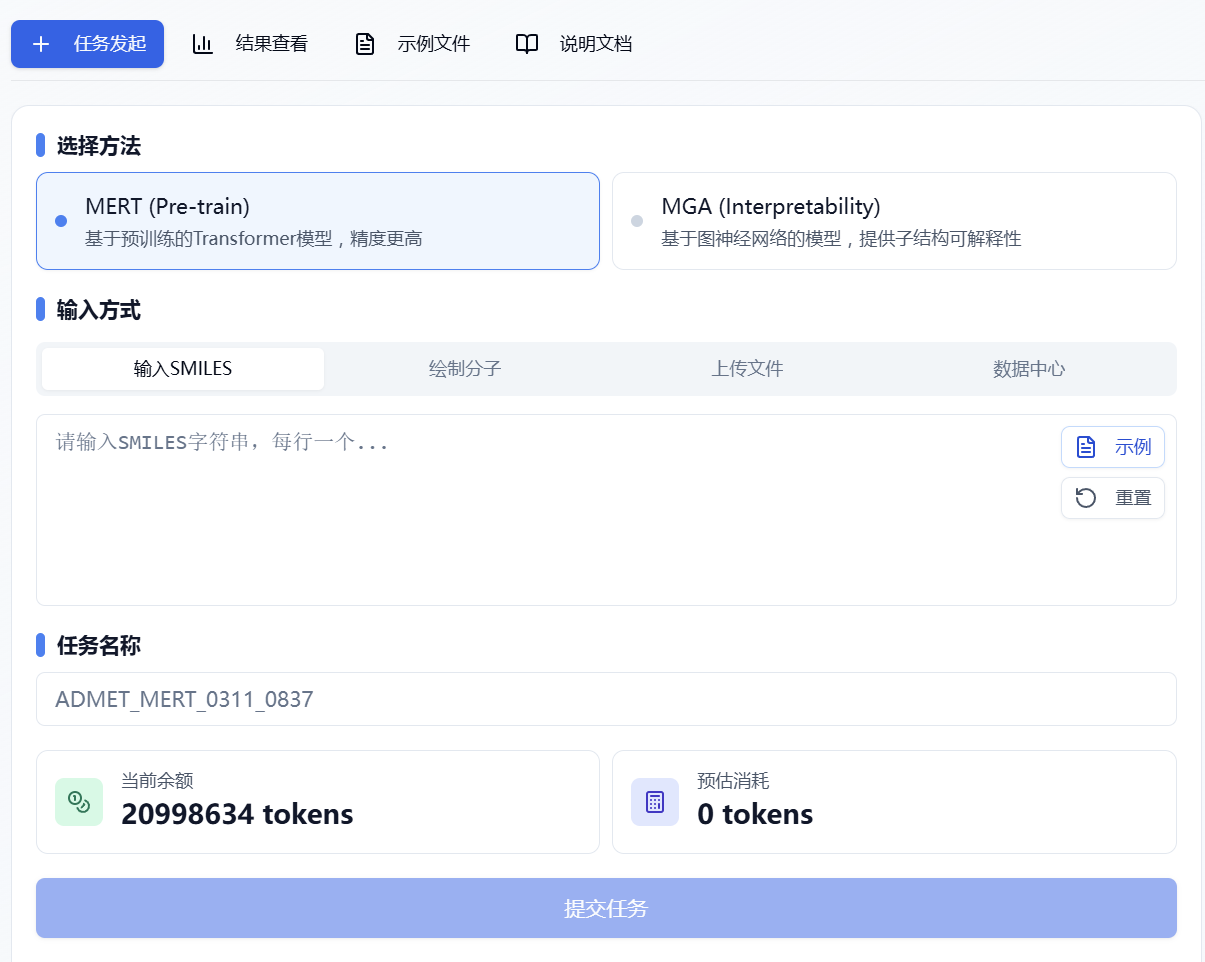
图 1. 创建 Inno-ADMET 任务页面
(1) 选择方法
- MERT(Pre-train):基于预训练的模型,模型的精度更高,预测能力更好,且速度快,计算一个分子只需 2.35ms;
- MGA(Interpretability):基于 GNN 子结构可解释性的 MGA 模型,模型预测效果不如 MERT(Pre-train),但该方法能够有效的计算子结构对预测结果的贡献度,有助于挖掘构效关系,在一定程度上可以指导结构优化。选择 MGA 进行计算时,有一个子结构可解释性的开关,由用户决定是否计算子结构可解释性。如打开该开关,系统将会计算子结构对属性的影响,但同时也会增加计算时间。
(2) 输入方式
平台提供了四种数据输入方式:输入 SMILES、绘制分子、上传文件和数据中心。
- 输入 SMILES
复选框选中“输入 SMILES”,在文本框中输入一个或多个 SMILES 表达式(用换行的方式输入多个 SMILES),该文本框中最多可输入 500 个 SMILES(超出上限可通过上传文件的形式提交任务)。
- 绘制分子
复选框选中“绘制分子”,点击打开分子编辑器进行分子绘制,画好以后点击右下角的“确认”即可。该模式下只支持画一个分子。
- 上传文件
复选框选中“上传文件”,通过点击下方按钮选择本地文件即可。选择完文件以后,右边将显示文件内容。 关于上传的文件:
当前支持的文件格式: .sdf/.csv;
文件大小不超过 10MB。
- 数据中心
复选框选中“数据中心”,通过点击下方按钮页面出现弹窗,点击文件名称来选择数据中心的数据。
(3) 运行进度和结果查看
提交任务后,页面会自动跳入当前页面的“结果查看”子页面中,您可以在该页面查看当前模块的任务运行状态(进度条),也可在右上角的“通知”下拉框中查看所有模块正在运行的任务。当数据量较大时,系统会分批计算,因此只要有一批数据算完后(整个任务还在运行中),即可点击“结果详情”按钮进入结果页面,查看当前已完成计算的预测结果列表(未完成计算的分子暂不显示),并且可以在当前页面通过刷新来获取最新算完的数据。
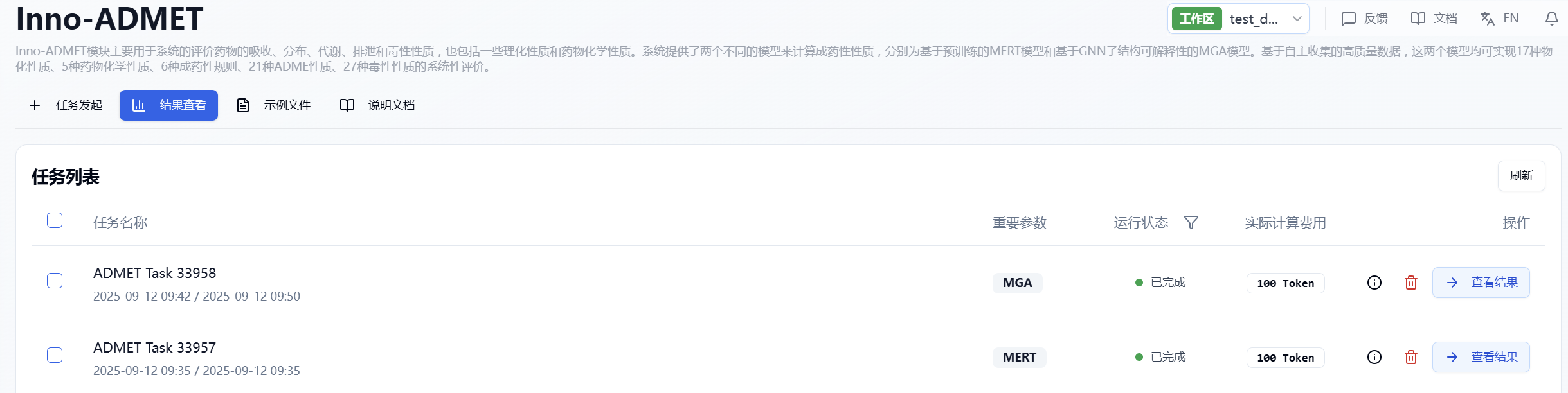
图 2. 查看结果
3. 结果分析
结果页面默认状态下展示的是表格形式(还可以切换为网格形式),此时您可以查看预测的所有性质,并对这些性质进行排序、筛选;同时为了方便用户直观的分析数据,我们给预测结果分配了一个颜色。
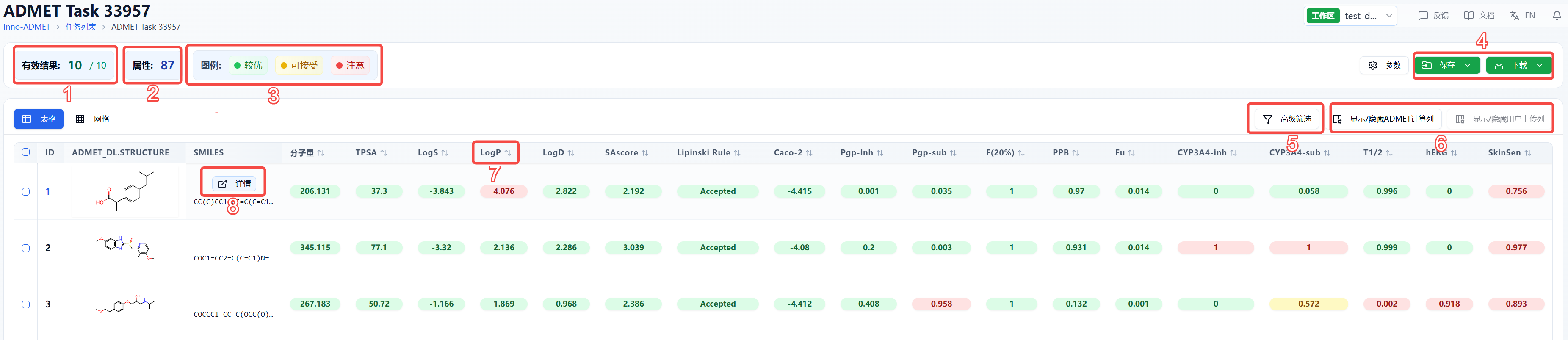
图 3. 结果页面功能分布
(1) 有效结果
有效结果格式为 当前表格显示的分子数/上传分子数。
(2) 属性
显示计算的属性总数,即87种。
(3) 图例
由于不同的性质有不同的建议取值区间,因此我们通过颜色对预测结果做了直观的评估。颜色设置的规则如下:
- 针对预测结果为 0-1 之间的性质:
P≤0.5,数值的底色为绿色,代表预测的化合物不属于该类别的化合物;
0.5<P<0.7,数值的底色为黄色,代表预测化合物有可能属于该类化合物;
P≥0.7,数值的底色为红色,代表预测的化合物很有可能属于该类化合物。
- 针对有最优区间的性质,如:
Fsp3 的最优取值为 Fsp3≥0.42,定义两个颜色,符合该阈值的为绿色,不符合的为红色;
Log S 的最优区间为-4~0.5,定义两个颜色,在区间内的为绿色,超出区间的为红色;
QED 的取值有三种定义:Attractive: > 0.67; unattractive: 0.49-0.67; too complex: < 0.34,按照该定义分配红绿黄的颜色即可。
通过以上颜色区分,您可以更直观的了解分子的整体评价结果。绿色背景越多,说明分子的 ADMET 性质越好,反之亦然。
(4) 保存/下载
点击保存/下载,系统将弹出下拉框让您选择保存/下载的文件格式(目前仅支持.csv/.sdf)。确定好保存/下载的文件格式后,需要选择保存/下载的行和列。保存/下载范围包括勾选的行--即表格首列的方框勾选分子;筛选后的行--即通过高级筛选得到的分子;所有行--即所有的分子;当前显示的列--即当前显示在页面上的列;所有列--即包括显示和未显示的所有列。系统将根据您的设置,保存相应的数据至数据中心,或下载数据至本地。
(5) 高级筛选
选择关注的属性进行筛选,可添加多个筛选条件进行组合筛选。
(6) 显示/隐藏列
显示/隐藏 ADMET 计算列,可对计算出的 ADMET 性质进行显示/隐藏;
显示/隐藏用户上传列,可显示/隐藏用户上传文件中原来就包含的列。
(7) 属性解释、排序
把鼠标移入每个性质的名称上,可查看该属性对应的解释;
点击性质的名称可重新排序,点击一次为升序,再点一次为降序,再点一次即恢复原始排序。
(8) 单个分子详情页
当您想查看某一个分子的所有性质时,可将鼠标移入表格区,通过点击浮现的详情按钮,即可进入分子详情页。MGA 模型相较于 MERT 模型多了子结构属性,如图 4 所示。
可在子结构属性下方的下拉框中选择您感兴趣的属性,如 hERG 毒性。Functional Group (FG) Mask、BRICS Substructure Mask、Murcko Substructure Mask 三者分别按照不同的规则划分子结构。FG & BRICS & Murcko Merge (Positive) 和 FG & BRICS & Murcko Merge (Negative) 是对三种规则的综合,分为了 Positive 正贡献和 Negative 负贡献。
如 Fig Legend 所示,颜色越蓝,说明正贡献越大;颜色越红,说明负贡献越大。
举例:hERG毒性预测为二分类模型,预测值越接近于1,说明更可能有毒;预测值越接近于0,说明更可能无毒。图 4 显示了 hERG 毒性的子结构结果。其中烷基为偏蓝色,即正贡献,会使预测值变大,更接近于1,也就是更可能使分子有毒;羧基为红色,即负贡献,会使预测值变小,更接近于0,也就是更可能使分子无毒。
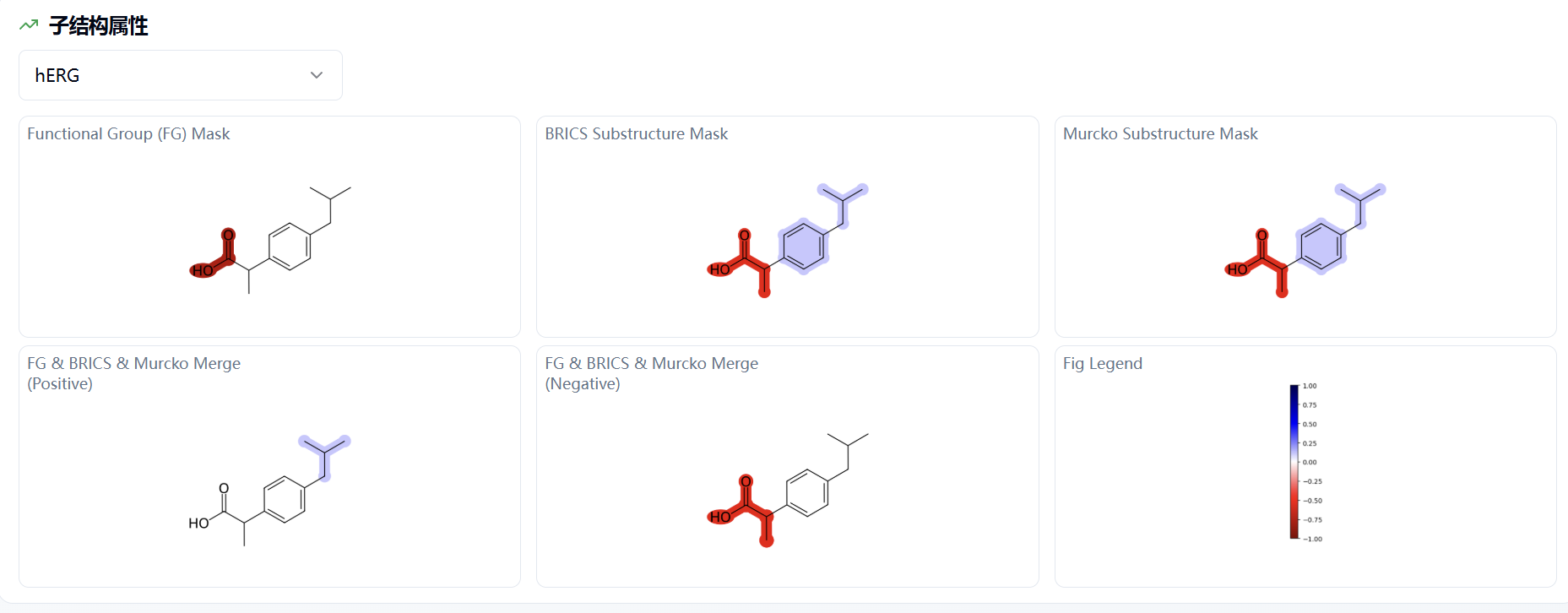
图 4. 分子详情页面-子结构属性
4. 相关算法介绍
系统提供了两个不同的模型来计算成药性性质,分别为基于预训练的 MERT 模型和基于 GNN 子结构可解释性的 MGA 模型。Inno-ADMET(MERT)和 Inno-ADMET(MGA)建模框架如图 5 和 6 所示。
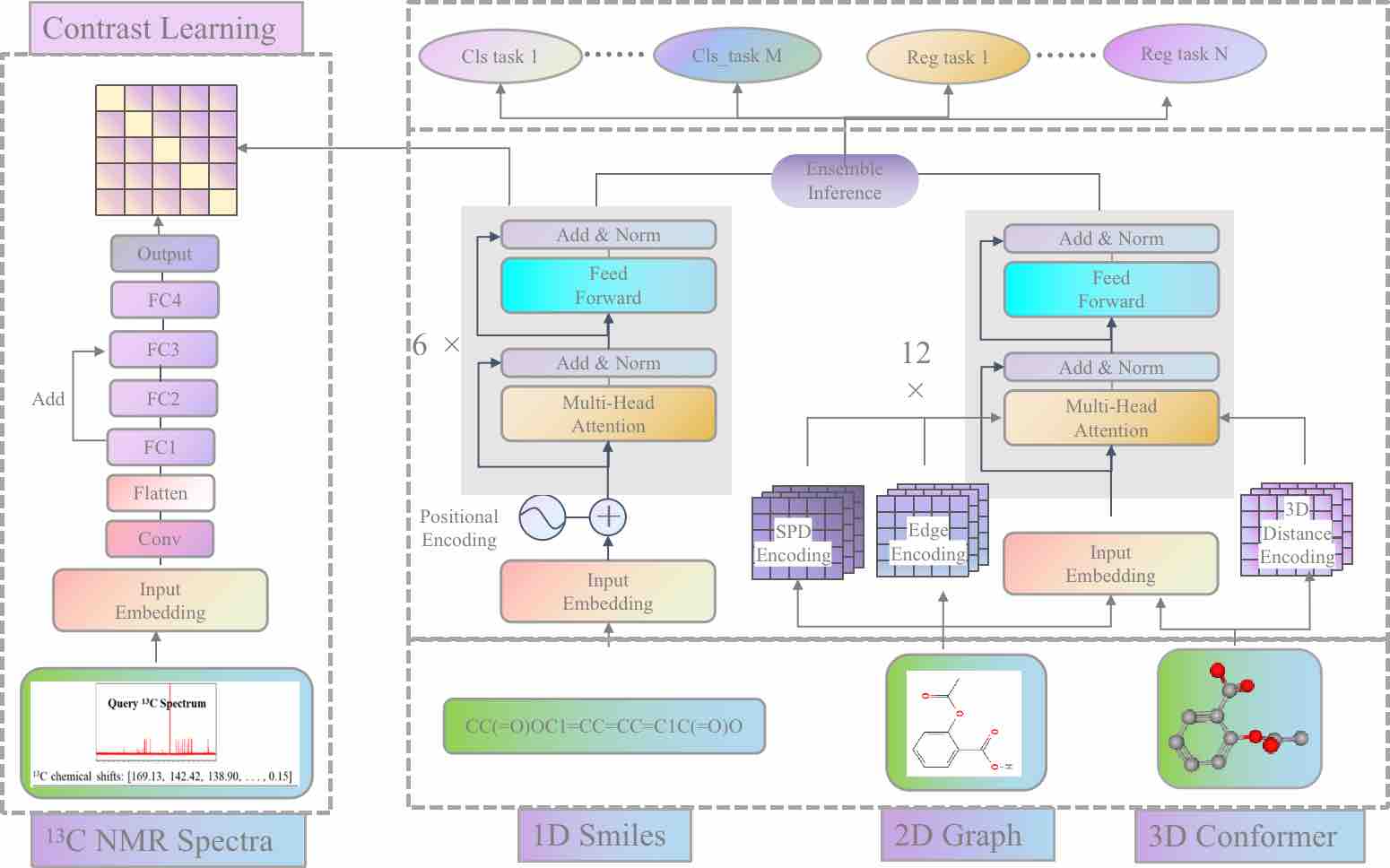
图 5. Inno-ADMET(MERT)建模框架
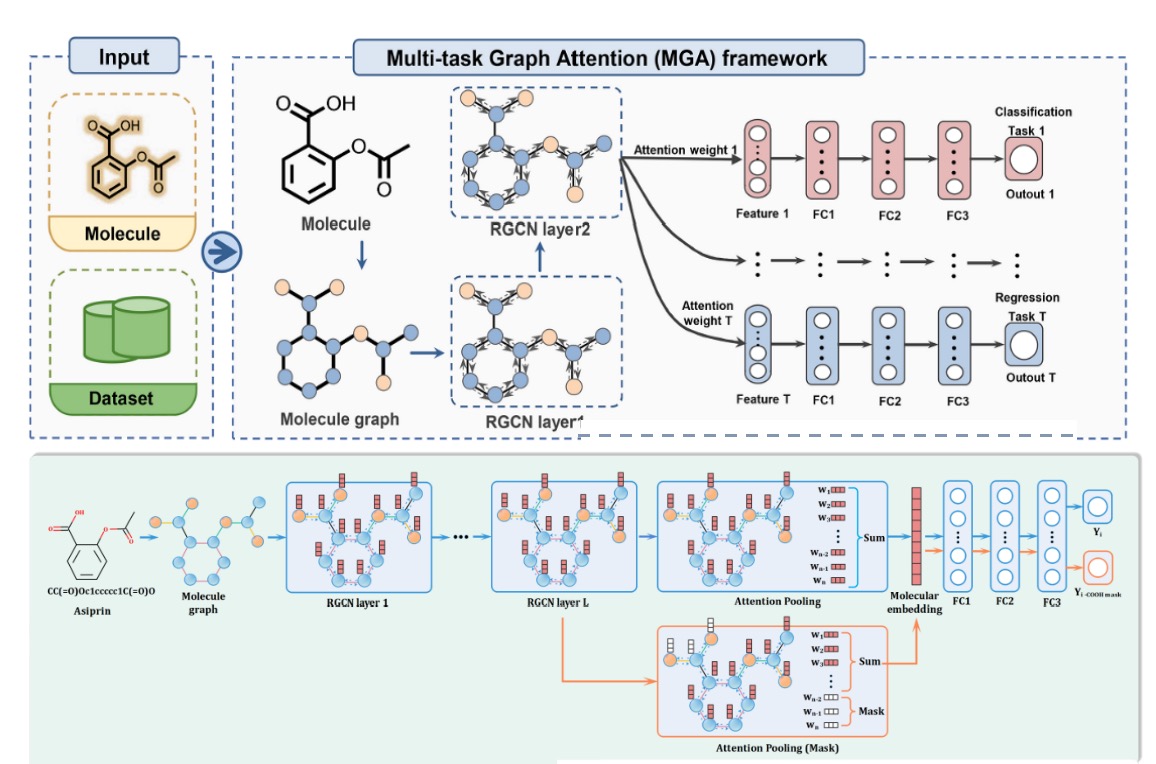
图 6. Inno-ADMET(MGA)建模框架
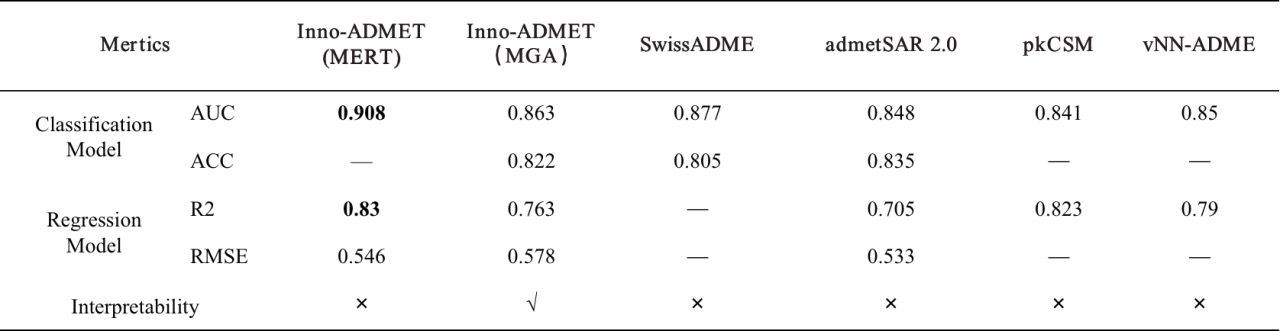
除了我们的 ADMET 模块,同类型计算 ADMET 性质的平台还有 SwissADME、admetSAR 2.0、FAF-Drugs4、pkCSM 和 vNN-ADME,我们详细比较了这些平台之间的差异,其详细信息汇总在表 1 中。经详细比较得知,这些平台工具各有侧重点,比如 SwissADME 可以提供 logP 和 logS 的多种计算方法以及各种药物相似性规则;admetSAR 2.0 包括最多样化的代谢特性;FAF-Drugs4 首次尝试在 ADMET 评估中加入毒物规则;而 vNN-ADME 中可用的预测性质相对有限。相比之下,ADMET 模块可用于预测分子质量的每个重要方面,涵盖药物化学家感兴趣的主要终点。尤其是平台提供的一些毒性子结构规则、毒性途径和一些药物化学性质预测是独一无二的工具。MERT 模型和 MGA 模型预测结果如表 2 所示。从模型评估指标上来看,Inno-ADMET (MERT) 比其他平台准确率更高;从结果可解释性的角度来看,Inno-ADMET (MGA) 更具优势。 另外从速度上来说,Inno-ADMET (MERT)的速度要优于 Inno-ADMET (MGA),Inno-ADMET (MERT)的速度达到了 2.35ms/分子。
表 1. ADMET 模块与其他基于 web 的工具的主要特性比较。“+”表示支持该特性,每多增加一个“+”表示支持度更高。

表 2. 各个平台的平均评估结果
5. 相关文献
[1] Chemistry-intuitive explanation of graph neural networks for molecular property prediction with substructure masking, Nature communications, 2023, 14, 2585.
[2] ADMETlab 2.0: an integrated online platform for accurate and comprehensive predictions of ADMET properties, Nucleic acids research, 2021, 49, W5-W14.
[3] ADMETlab: a platform for systematic ADMET evaluation based on a comprehensively collected ADMET database, Journal of cheminformatics, 2018, 10, 29.
